回顾使用3D体外肿瘤类器官鉴别癌症生物标志物的原因和途径。
生物标志物在肿瘤药物开发中的价值
癌症是一种极具异质性的疾病,每个患者对同一治疗方法的反应大相径庭。因此,约97%的肿瘤临床试验遭遇失败也就不足为奇了。但是,当研究使用生物标志物策略选择患者时,成功率较高。
近年来,癌症生物标志物的使用取得了较大进展,包括FDA批准基于特定肿瘤生物标志物而非肿瘤位置或肿瘤起源部位使用帕博利珠单抗(Keytruda®, Merck)和拉罗替尼(Vitrakvi®, Bayer)治疗癌症患者的重大进展。
目前,6000多种研究药物正在开发中,因此非常需要鉴别预测性生物标志物,以便对患者进行分层,从而在提高患者安全性的同时提供治疗成功的最佳机会。在药物开发过程的早期,开发稳健和敏感的生物标志物有助于建立一个由生物标志物引导的方法,在早期阶段鉴别出最有前景的候选疗法,并为特定的患者群体和癌症适应症定制新疗法。
为什么使用肿瘤类器官鉴别癌症生物标志物?
仍需使用经改进的工具来发现新的生物标志物,这对改善癌症护理至关重要。为了鉴别出生物标志物,肿瘤模型必须忠实地再现原始肿瘤,预测患者的体内临床反应,且适用于高通量药物筛选(HTS)。
肿瘤类器官为生物标志物的鉴别提供了新一代的方法。特别是,Hubrecht Organoid Technology (HUB)已经开发了优化方案,以便从多种原发性人类癌症中生成肿瘤类器官。利用HUB协议建立的肿瘤类器官再现了其亲代肿瘤的基因组、形态和病理生理特性,且这些特性在体外被无限期地维持。这为生物标志物鉴别提供了高度临床相关的3D体外肿瘤模型。
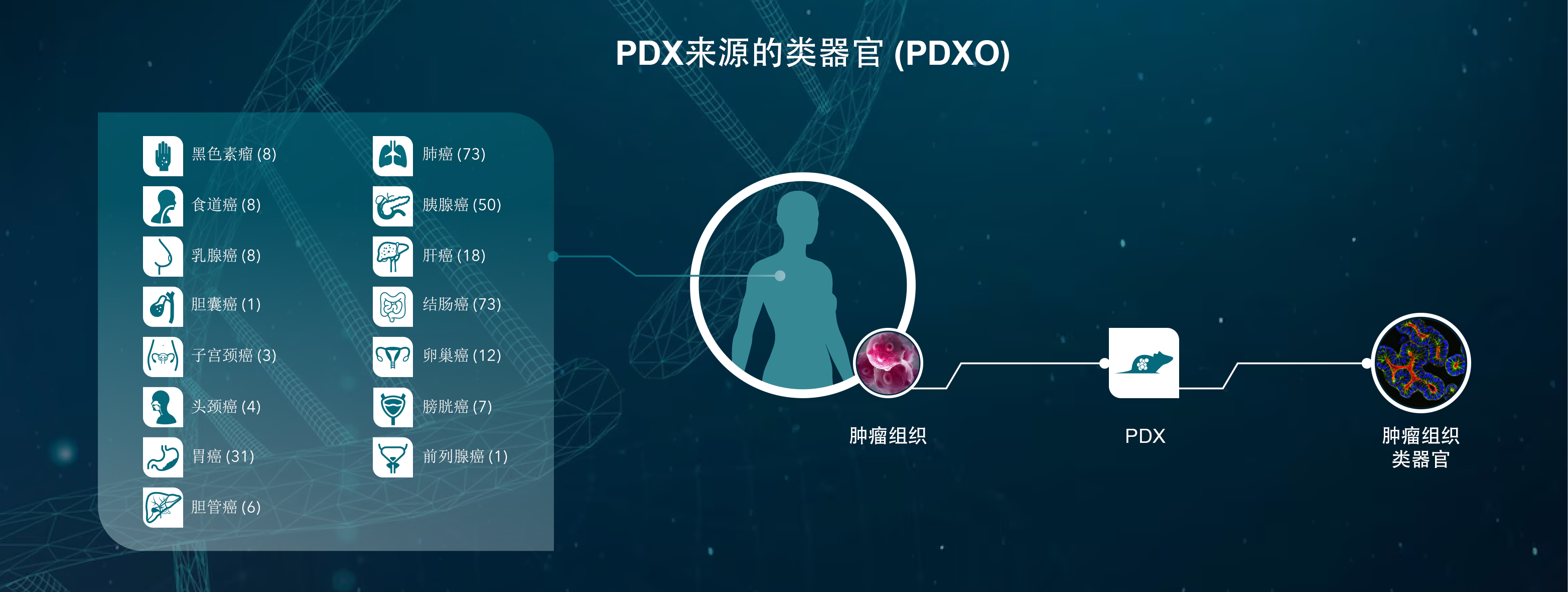
同时,已建立患者相关肿瘤类器官的生物样本库,以捕获患者群体中存在的异质性谱。由于这些体外模型适用于高通量药物筛选,它们为研究反应的生物标志物提供了可能性。
使用肿瘤类器官鉴别癌症生物标志物的途径
由于肿瘤类器官为患者高度相关的体外模型,因此它们提供了通常在标准2D或3D培养筛选中无法获得的独特机会。但是,基于类器官的药物开发平台需满足一系列的要求,才能提供显著的效益,并充分利用这些先进的临床前模型。
较大模型生物样本库
为了真实地反映患者群体的多样性,应广泛收集肿瘤类器官模型。收集应包括每个组织类型和多个癌症适应症的多个模型,以涵盖各种突变和药理学特征。这为同时评估多个模型的反应和鉴别预测性生物标志物提供了机会。
良好注释的收集
肿瘤类器官的效能不仅仅体现在数量上。为了提供信息,应通过基因组分析数据对基因组分析数据进行充分地注释。然后,新药物或再利用药物基因印记和生物标志物的发现可基于可用的基线基因组数据。
稳健的体外测定
经有效设计后,基于类器官的筛选平台需通过经确定的读取数据进行稳健的测定。这包括检测类器官细胞杀伤的细胞毒性测定或评估免疫肿瘤药物的经验证测定。这为生成的数据提供了信心,并实现对药物靶点的敏感者和非敏感者模型的鉴别。
执行高通量筛选(HTS)的能力
这允许对大量模型或药物(及其组合)进行快速筛选,并提供了大量的重复(“n”),以实现强大的统计分析。
生物信息学/计算机支持
需具备生物信息学能力,以处理通过HTS获得的信息
后续体内模型
后续体内模型需具有可用性,以检测假设或转移到更复杂的系统。在理想的情形下,体内模型和类器官模型来自同一患者,尽管这是非常罕见的情况。另外,匹配的类器官和PDX模型提供了一个在预测患者反应的体内系统中验证体外数据的独特机会。这些匹配的系统可对生物标志物进行进一步验证,因为肿瘤反应的某些方面无法在体外再现
结论
在临床前人群研究中使用肿瘤类器官鉴别癌症生物标志物,提供了一种创新的生物标志物发现方法。由于存在具有明显特征和注释的肿瘤类器官生物样本库,且这些肿瘤类器官再现了在患者人群中观察到的异质性,使之成为可能。
此外,肿瘤类器官还适用于可验证生物标志物表达和患者药物反应的回顾性分析。由于它们是一个体外平台,因此可用于高通量药物筛选,以便基于经鉴别生物标志物的分层检测药物反应。